はじめに
科学の再現性が改めて重視される世にあって、Rmarkdownの便利さもより強く認識される日々です。
例えば、@kohske さんが「再現可能性のすゝめ」というRmd本を執筆しました。
https://qiita.com/kohske/items/3e8c02e9598c6d230a47
ちなみにまだ買ってもいません…………。
このため、同書で言及されているかは知りませんが、Rmdを使って再現性を確保していくにあたって、問題となりうることの一つに
.Rprofile
があります。
これは、R起動時に実行したしスクリプトを書いておくところで、
- CRANミラーの選択
- ライブラリの読み込み
- メッセージの表示
などなど、いろいろなことができます。
.Rprofileをホームディレクトリに置いて、オレオレR環境を整備しておくと便利なのですが、Rmdのknit時にも読み込まれてしまうため、異なる環境で同じRmdファイルをknitしても同じ出力が得られるとは限りません。
しかし、.Rprofileをうまく使うと、Rmdファイルを作成する度に読み込むパッケージを羅列する必要がなくなるので便利です。
どうしたら、再現性を保ちつつ、.Rprofileを運用できるのでしょうか。
working directoryに.Rprofileを置く
working directoryに.Rprofileを置くと、それはホームディレクトリ下のものよりも高い優先順位を持ちます。
RStudio上でプロジェクトを管理しているならば、プロジェクトディレクトリ = working directoryなので、そこに.Rprofileをコピーするといいでしょう。
ディレクトリを丸ごと別環境に移しても.Rprofileの内容が再現されます。
これで子chunkだけを実行する時も、必ず実行したいコードは.Rprofileに仕込めばOKですね!
Rmd内に、.Rprofileをインポートする
発展的には、プロジェクトディレクトリに置いた.RprofileをRmdファイルにインポートすると、出力(htmlなど)で.Rprofileの内容も確認できて便利です。
これには少々工夫がいります。
source('.Rprofile') では、.Rprofile中のソースコードが出力に表示されないためです。
child = '.Rprofile' も.RprofileがRmdファイルではないがために愉快な出力になります。
そこで下記のようにします
.Rprofileの編集
冒頭に ## @knitr rprofile を追記し、Rmdから.Rprofileを取り込めるようにしましょう(参考)。
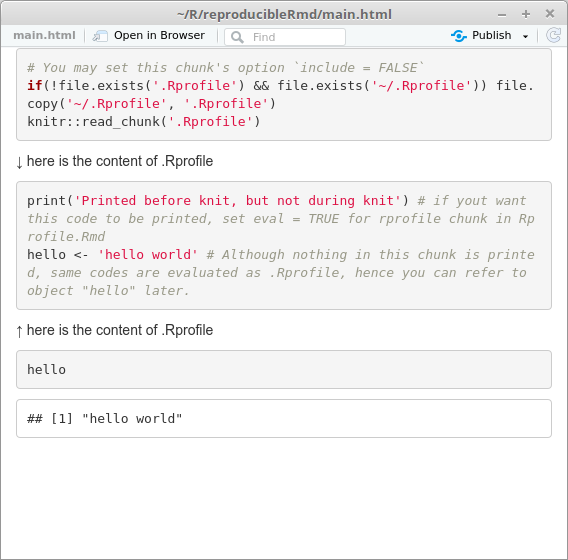
print('Printed before knit, but not during knit') # if yout want this code to be printed, set eval = TRUE for rprofile chunk in Rprofile.Rmd
hello <- 'hello world' # Although nothing in thi chunk is printed, same codes are evaluated as .Rprofile, hence you can refer to object "hello" later.
繰り返しになりますが、プロジェクトディレクトリに置いておきます。
.Rprofileを取り込むRmdファイルを作成
下記のように Rprofile.Rmd を作成しましょう。
```{r, include = FALSE}
knitr::read_chunk("script.R")
```
↓ here is the content of .Rprofile
```{r rprofile eval = TRUE}
```
↑ here is the content of .Rprofile
ここで何をしているかは @yu-iskw さんの
を参考にしてください。
メインのRmdからrprofile.Rmdを呼び出す
```{r child = 'Rprofile.Rmd'}
```
knitする
出力はこんな感じ
ちなみに、Rmdを子chunkに分割した時、子chunkで child = 'rprofile.Rmd' を行う必要はありません。
そうせずとも、テスト用の子chunkをknitした時も、.Rprofileの読み込みは行われます。
.Rprofileの中身を見せる必要があるのは、親chunkに出力だけだと思います。