はじめに
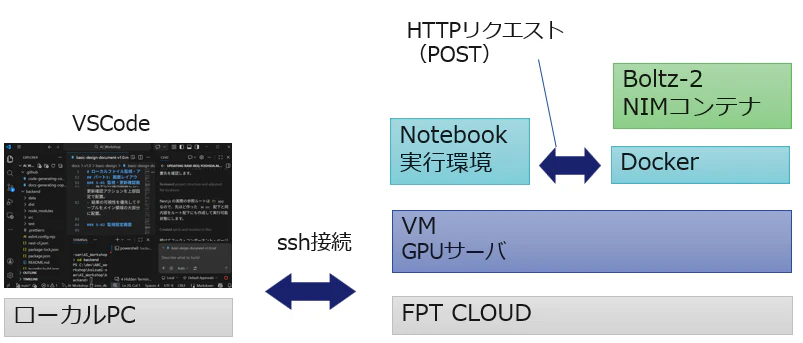
GPUは「ローカルLLM」や「フィジカルAI」の文脈で語られがちです。今回は創薬・バイオ用途として、FPT CLOUDのGPUサーバが手間なく利用できるかを確認します。
今回は、創薬向けソリューションである "Boltz-2" のNIMコンテナをデプロイして、生体分子の結合構造予測を試してみます。
追記:2026年4月22日
下記ではPaaSである、FPT AI FACTORYを使ったBoltz-2 NIMコンテナ使用方法についてまとめました。
Boltz2とは?
今回デプロイするNIMコンテナの "Boltz-2" は、生体分子(タンパク質と薬の分子)がどのように結びつくかをAIで予測するツールです。
具体的には下記のような予測を高速・高精度で実現します。
- タンパク質やDNAと薬の分子がどのような立体構造で結合するか
- タンパク質やDNAと薬の分子の結合の強さ(結合親和性という)
補足:NIMとは?
NVIDIA Inference Microservices の略で、NVIDIAのGPUに最適化された推論基盤を提供するマイクロサービス(コンテナとして配布)のことです。
これをデプロイすることで素早くLLMやTTS(テキストから音声を生成)などのサービスを素早く・運用しやすい形で提供することができます。
検証のゴール
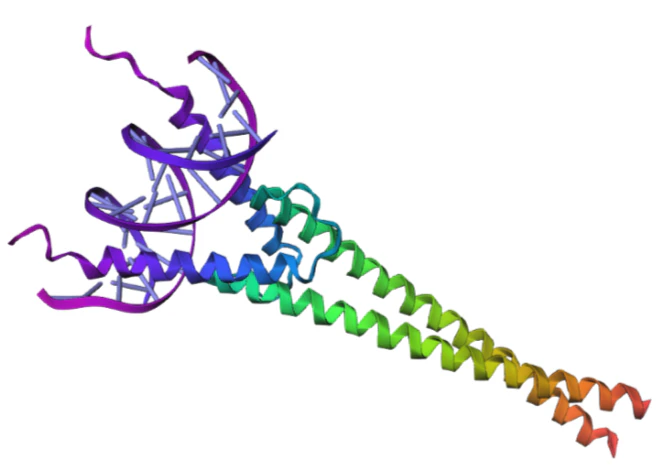
FPT CLOUDにデプロイしたBoltz-2を使い、分子結合の予測を実行し、最終的に3Dで可視化できる状態にします。
■生成物のイメージ
- 必要なもの
- FPT CLOUDアカウント
- NGCのAPIキー(取得方法は後述)
- 分子結合予測までのステップ
- NGCのAPIキーを取得する
- FPT CLOUDでGPUサーバを立ち上げる
- Boltz2 NIMコンテナのデプロイ
- サンプルプログラムの実行
最低システム要件
公式ドキュメントによると、最低限下記のスペックが必要です。
- CPU コア : 12
- RAM : 64 GB
- SSD Strage : 80 GB
- GPUメモリ: 48 GB
構成
手順
①NGCのAPIキーを取得する
下記リンクからNGCにログインします
https://ngc.nvidia.com/signin
ログイン後、画面右上に表示されている自分のアカウントをクリックし、[Setup]をクリック
下記のように必要事項を記入し、[Generate Personal Key]をクリック
※Key NameとExpirationは任意です

nvapiから始まるAPIキーが発行されるので、コピーします
②FPT CLOUDでGPUサーバを立ち上げる
下記リンクから FPT CLOUDのコンソールにアクセスし、GPUサーバを立ち上げます
ログイン:https://console.fptcloud.com/login/select-method
※ポータルサイトはこちら:https://fptcloud.com/ja/
③ Boltz-2 NIMコンテナをデプロイする
sshでGPUサーバに接続し、取得したAPIキーを設定する
export NGC_API_KEY=<ここに取得したAPIキーをセットする>
DockerでNGCにログインする
$oauthtokeは特殊な名前で、APIキーを使って認証することを表しています。
echo "$NGC_API_KEY" | docker login nvcr.io --username '$oauthtoken' --password-stdin
NIMキャッシュを作成する
export LOCAL_NIM_CACHE=~/.cache/nim
mkdir -p ${LOCAL_NIM_CACHE}
chmod 777 ${LOCAL_NIM_CACHE}
NIMコンテナを起動する
docker run --rm --name boltz2 --runtime=nvidia \
--shm-size=16G \
-e NGC_API_KEY \
-v $LOCAL_NIM_CACHE:/opt/nim/.cache \
-p 8000:8000 \
nvcr.io/nim/mit/boltz2:1.5.0
④サンプルのノートブックを実行する
サンプルのノードブックをダウンロードする
- 以下ドキュメントの “Example Notebooks” に2つサンプルがありますが、今回は 2つ目 を使用します。
https://docs.nvidia.com/nim/bionemo/boltz2/latest/inference.html#example-notebooks

VSCodeでGPUサーバに接続し、ダウンロードしたipynbファイルをアップロードする
仮想環境を立ち上げる
Python3 –m venv venv-Boltz2
source venv-Boltz2/bin/activate
ノートブックのセルを上から順に実行する
※プログラムを実行する過程で httpx と py3Dmol がインストールされます。
最終的に、、、
ノートブックを上から順に実行し、🎨 Interactive 3D Visualizationのセクションを実行すると、このようにDNAとタンパク質の構造を3Dで予測・可視化することができました!!!
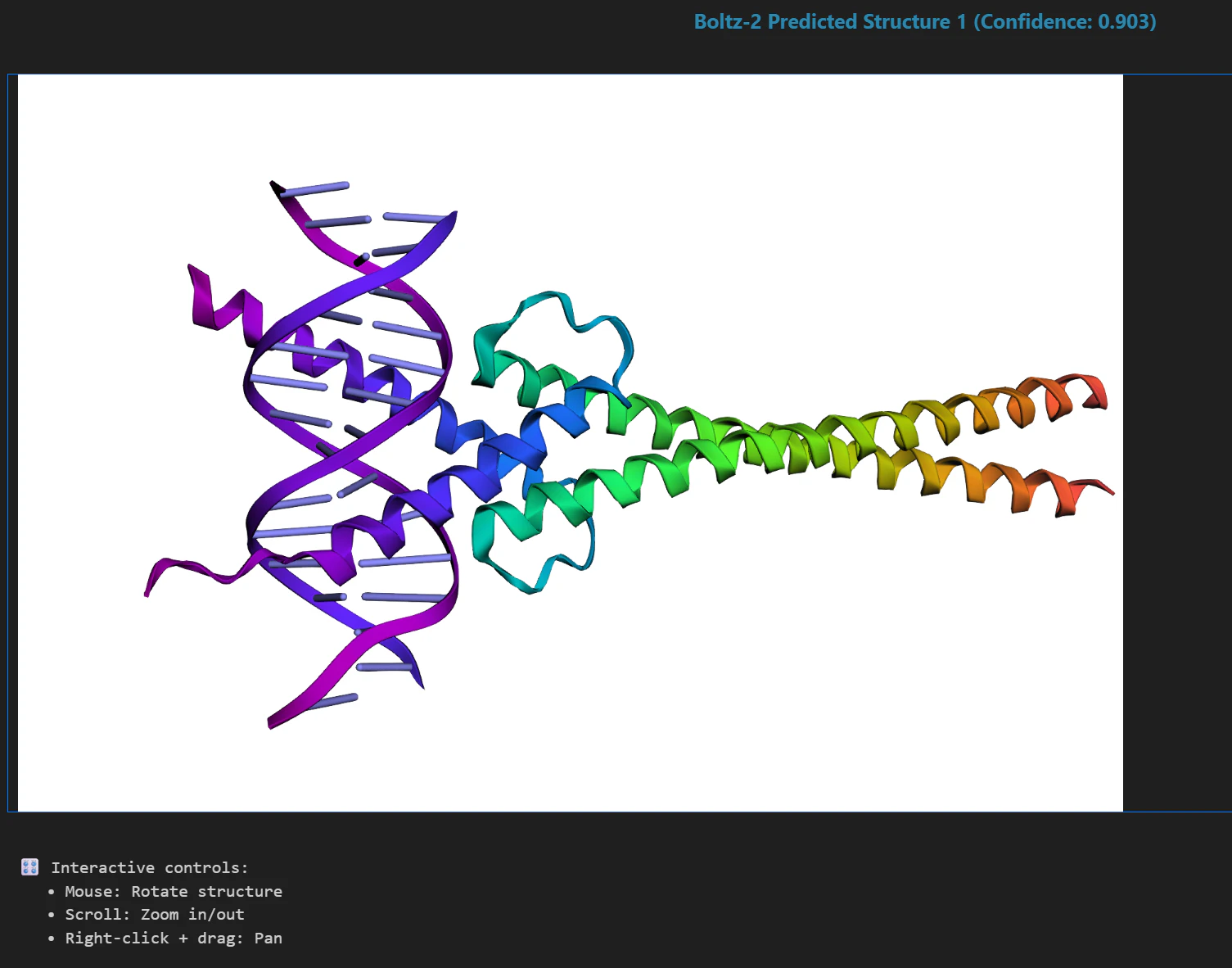
マウスの操作で拡大縮小・回転などの操作が行えます。
DNAやたんぱく質の構造はどこで定義されている?
サンプルコードを見ていくと request_data内で分子の情報(DNA配列・タンパク質配列など)を定義しています。
# Example protein sequence
# sequence = "MKTVRQERLKSIVRILERSKEPVSGAQLAEELSVSRQVIVQDIAYLRSLGYNIVATPRGYVLAGG"
# Prepare the request payload according to the API schema
request_data = {
"polymers": [
{
"id": "A",
"molecule_type": "protein",
"sequence": "MGREEPLNHVEAERQRREKLNQRFYALRAVVPNVSKMDKASLLGDAIAYINELKSKVVKTESEKLQIKNQLEEVKLELAGRLEHHHHHH",
"cyclic": False,
"modifications": [] # No modifications
},
{
"id": "B",
"molecule_type": "protein",
"sequence": "MGREEPLNHVEAERQRREKLNQRFYALRAVVPNVSKMDKASLLGDAIAYINELKSKVVKTESEKLQIKNQLEEVKLELAGRLEHHHHHH",
"cyclic": False,
"modifications": [] # No modifications
},
{
"id": "C",
"molecule_type": "dna",
"sequence": "TGGGTCACGTGTTCC",
"cyclic": False,
"modifications": [] # No modifications
},
{
"id": "D",
"molecule_type": "dna",
"sequence": "AGGAACACGTGACCC",
"cyclic": False,
"modifications": [] # No modifications
}
],
詰まりやすいポイントと解決策
- NGCのAPIキー取得までが少し複雑です。
→ 上記ドキュメントを見ながら、該当する取得方で進めるのが確実です。
検証結果・感想
手順としては大きく4ステップ(APIキー取得 → VM作成 → NIM起動 → ノートブック実行)で、Boltz-2を想像以上にスムーズにデプロイできました。
「創薬・バイオ系は準備が作業が重いのでは?」と思っていましたが、NIMのおかげでかなりあっさり動かせたのが印象的です。
FPT CLOUDを試したくなったら
FPT CLOUDでNIMコンテナをデプロイしてみたい、GPUサーバとして使ってみたいという方はFPTスマートクラウドジャパンまでお問い合わせください。
参考