はじめに
本記事は以下の人を対象としています.
- 筋骨格シミュレータに興味がある人
- MuJoCoに興味がある人
本記事では3_Analyse_movements.ipynbをGoogle Colabで実行した際の手順と結果に関してまとめる.
MyoSuiteとは
MuJoCoを学習モジュールとして組み込んだ筋骨格シミュレータ
2024年にICRAにてworkshopを展開
https://sites.google.com/view/myosuite/myosymposium/icra24
Tutorial Notebook
実施事項
Tutorialに記載のコードを1つずつ試して, Errorになったところは都度修正版を記載する.
ライブラリのinstallと環境設定
!pip install -U myosuite
!pip install tabulate matplotlib torch gym==0.13 git+https://github.com/aravindr93/mjrl.git@pvr_beta_1vk
!pip install scikit-learn
%env MUJOCO_GL=egl
ライブラリのimportと結果表示の関数
from myosuite.utils import gym # importが上手くいくと"MyoSuite:> Registering Myo Envs"と表示される
import skvideo.io
import numpy as np
import os
from IPython.display import HTML
from base64 import b64encode
def show_video(video_path, video_width = 400):
video_file = open(video_path, "r+b").read()
video_url = f"data:video/mp4;base64,{b64encode(video_file).decode()}"
return HTML(f"""<video autoplay width={video_width} controls><source src="{video_url}"></video>""")
modelのloadとpolicyの準備
# stable-baselines3のinstall
!pip install stable-baselines3
from stable_baselines3 import PPO
env = gym.make('myoElbowPose1D6MRandom-v0')
env.reset()
pi = PPO("MlpPolicy", env, verbose=0)
pi.learn(total_timesteps=1000)
stable_baselines3についてはnpakaさんの資料を参照
actionによる筋負荷データの出力
frames = []
data_store = []
for _ in range(10): # 10 episodes
for _ in range(100): # 100 samples for each episode
frame = env.sim.renderer.render_offscreen(
width=400,
height=400,
camera_id=0
)
frames.append(frame)
o = env.get_obs()
a = pi.predict(o)[0]
next_o, r, done, *_, ifo = env.step(a) # take a random action
data_store.append({"action":a.copy(),
"jpos":env.sim.data.qpos.copy(),
"mlen":env.sim.data.actuator_length.copy(),
"act":env.sim.data.act.copy()})
env.close()
os.makedirs('videos', exist_ok=True)
# make a local copy
skvideo.io.vwrite('videos/temp.mp4', np.asarray(frames),outputdict={"-pix_fmt": "yuv420p"})
show_video('videos/temp.mp4')
残タスク
- action, jpos, mlen, actがそれぞれ何を示すのか記載
出力結果
解析結果の表示
import matplotlib.pyplot as plt
from sklearn.decomposition import NMF
def VAF(W, H, A):
"""
Args:
W: ndarray, m x rank matrix, m-muscles x activation coefficients obtained from (# rank) nmf
H: ndarray, rank x L matrix, basis vectors obtained from nmf where L is the length of the signal
A: ndarray, m x L matrix, original time-invariant sEMG signal
Returns:
global_VAF: float, VAF calculated for the entire A based on the W&H
local_VAF: 1D array, VAF calculated for each muscle (column) in A based on W&H
"""
SSE_matrix = (A - np.dot(W, H))**2
SST_matrix = (A)**2
global_SSE = np.sum(SSE_matrix)
global_SST = np.sum(SST_matrix)
global_VAF = 100 * (1 - global_SSE / global_SST)
local_SSE = np.sum(SSE_matrix, axis = 0)
local_SST = np.sum(SST_matrix, axis = 0)
local_VAF = 100 * (1 - np.divide(local_SSE, local_SST))
return global_VAF, local_VAF
act = np.array([dd['act'] for dd in data_store])
VAFstore=[]
SSE, SST = [], []
sample_points = [1,2,3,4,5,10,20,30]
for isyn in sample_points:
nmf_model = NMF(n_components=isyn, init='random', random_state=0);
W = nmf_model.fit_transform(act)
H = nmf_model.components_
global_VAF, local_VAF = VAF(W, H, act)
VAFstore.append(global_VAF)
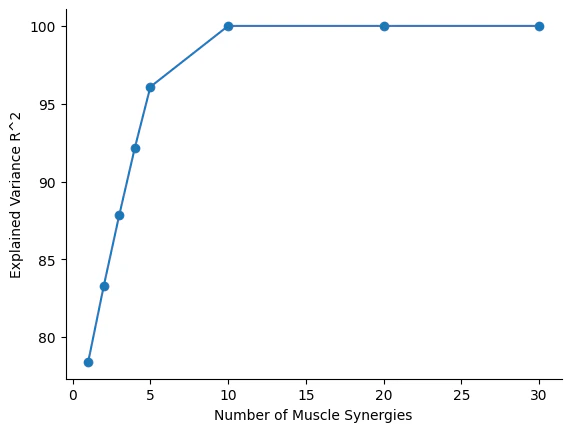
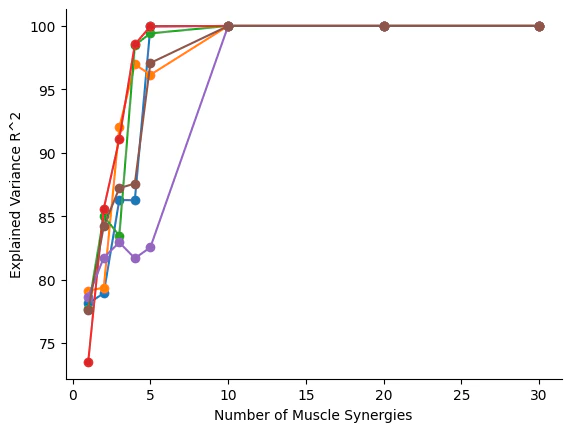
plt.plot(sample_points,VAFstore,'-o')
plt.xlabel('Number of Muscle Synergies')
plt.ylabel('Explained Variance R^2')
plt.gca().spines['top'].set_visible(False)
plt.gca().spines['right'].set_visible(False)
-
sample_pointsはNon-negative Matrix Factorization(NMF)実行時の次元数- 一応>1000でも実行はできる
- Muscle Synergyとは筋グループの数
-
sample_pointsの値が増えるということは筋グループの数が増えるということ - 今回だとMuscle Synergyは10未満が適度に分解されていい値?
-
参考資料