PCの余剰の計算リソースを提供することで、どなたでも新型コロナウイルスの研究を支援可能です。
間違い晒し
2020/3/28タイトルを一部修正
不正確な表記・記述をしていました。ごめんなさい。
修正前
COVID-19(新型コロナウイルス)
修正後
COVID-19(新型コロナウイルス感染症)
COVID-19:
- Coronavirus disease 2019
- 新型コロナウイルス感染症
- 2019新型コロナウイルスによる急性呼吸器疾患
SARS-CoV-2:
- 新型コロナウイルス
- SARSコロナウイルス-2
- Severe acute respiratory syndrome coronavirus 2(直訳すると『重症急性呼吸器症候群コロナウイルス2』)
出典:
https://ja.wikipedia.org/wiki/2019新型コロナウイルスによる急性呼吸器疾患
https://ja.wikipedia.org/wiki/2019新型コロナウイルス
https://en.wikipedia.org/wiki/Severe_acute_respiratory_syndrome_coronavirus_2
AIDS と HIV みたいな使い分け。
「コロナウイルス」の「コロナ」について
名前
「コロナウイルス」の名称はラテン語のcorona(コロナ)およびギリシャ語の王冠または光冠(丸い光の輪)、花冠を意味する κορώνη(korṓnē コロネ)に由来する[8][9]。
この名称は電子顕微鏡によるビリオン(感染性を有するウイルス粒子)の特徴的な外観に由来する。ビリオンは大きな球状の表面突起の縁をもち、樹冠や太陽コロナを思わせる像をつくる。この形態はウイルスのスパイク (S) ペプロマーによってつくられる。ペプロマーはウイルスの表面にあるタンパク質で、宿主の向性を決定する。
Folding@home や Rosetta@home はペプロマー(スパイク状の糖タンパク質)の構造解析辺りをやっているのかな?
画像出典:https://commons.wikimedia.org/wiki/File:3D_medical_animation_corona_virus.jpg
Folding@home のインストール
macOS
公式サイトよりダウンロード&インストール、もしくは Homebrew で
brew cask install folding-at-home
Windows
公式サイトよりダウンロード&インストール、もしくは Chocolatey で
choco install fah
FreeBSD
pkg install linux_base-c7
cd /usr/ports/biology/linux-foldingathome/ && make install clean
※ GhostBSD の場合の Ports
https://wiki.ghostbsd.org/index.php/Ports
https://wiki.ghostbsd.org/index.php/Using_the_Ports_Collection
Message from linux_base-c7
Some programs need linprocfs mounted on /compat/linux/proc. Add the
following line to /etc/fstab:
linprocfs /compat/linux/proc linprocfs rw 0 0
Then run "mount /compat/linux/proc".
Some programs need linsysfs mounted on /compat/linux/sys. Add the
following line to /etc/fstab:
linsysfs /compat/linux/sys linsysfs rw 0 0
Then run "mount /compat/linux/sys".
Some programs need tmpfs mounted on /compat/linux/dev/shm. Add the
following line to /etc/fstab:
tmpfs /compat/linux/dev/shm tmpfs rw,mode=1777 0 0
Then run "mount /compat/linux/dev/shm".
出典:インストール時のメッセージ
Getting Start with F@H
Quick start
===========
Here is a list of steps to quickly get started with Folding@home on FreeBSD:
1. Mount linprocfs(5) in /compat/linux/proc.
2. Mount linsysfs(5) in /compat/linux/sys.
3. Consider setting the user name and the team ID (e.g., "11743")
in /usr/local/etc/fahclient/config.xml.
4. Enable the fahclient service:
sysrc fahclient_enable="YES"
5. Start the service:
service fahclient start
At this point, the daemon should be up and folding.
Additional notes
================
- The current status of folding can be inspected by running
the following command:
service fahclient log
- The default working directory for fahclient is /var/db/fahclient.
In order to function properly, fahclient requires its working directory
to be on a partition/dataset with execute permissions on. For example
if /var/db is on a ZFS dataset with exec=off, then /var/db/fahclient
needs to have exec=on.
Note, that usually the permissions are on unless the system
configuration was modified by the administrator.
- The ID of the FreeBSD team is 11743. In order to join the team
add the following line to /usr/local/etc/fahclient/config.xml:
<team value="11743"/>
The service has to be restarted to pick up the change.
Statistics for the FreeBSD team can be viewed here:
https://stats.foldingathome.org/team/11743
- More information about configuring and running the Folding@home
software is available on those websites:
- https://foldingforum.org/
- https://foldingathome.org/support/faq/
===> SECURITY REPORT:
This port has installed the following files which may act as network
servers and may therefore pose a remote security risk to the system.
/usr/local/bin/FAHClient
This port has installed the following startup scripts which may cause
these network services to be started at boot time.
/usr/local/etc/rc.d/fahclient
If there are vulnerabilities in these programs there may be a security
risk to the system. FreeBSD makes no guarantee about the security of
ports included in the Ports Collection. Please type 'make deinstall'
to deinstall the port if this is a concern.
For more information, and contact details about the security
status of this software, see the following webpage:
http://folding.stanford.edu/
出典:インストール時のメッセージ
※ rc スクリプトを直接叩く場合、/usr/local/etc/rc.d/fahclient start等とする。
BOINC のインストール(Rosetta@home用)
macOS
公式サイトよりダウンロード&インストール、もしくは Homebrew で
brew cask install boinc
Windows
公式サイトよりダウンロード&インストール、もしくは Chocolatey で
choco install boinc
FreeBSD
pkg install boinc-client
boinc-client の開始
sysrc boinc_client_enable="YES"
/usr/local/etc/rc.d/boinc-client start
/usr/local/etc/rc.d/boinc-client status
Folding@home への参加
Folding@home への参加の流れ
グラフィカルユーザーインターフェイス
※ FAHViewer で作業中の分子のモデルを表示できます。
Web インターフェイス
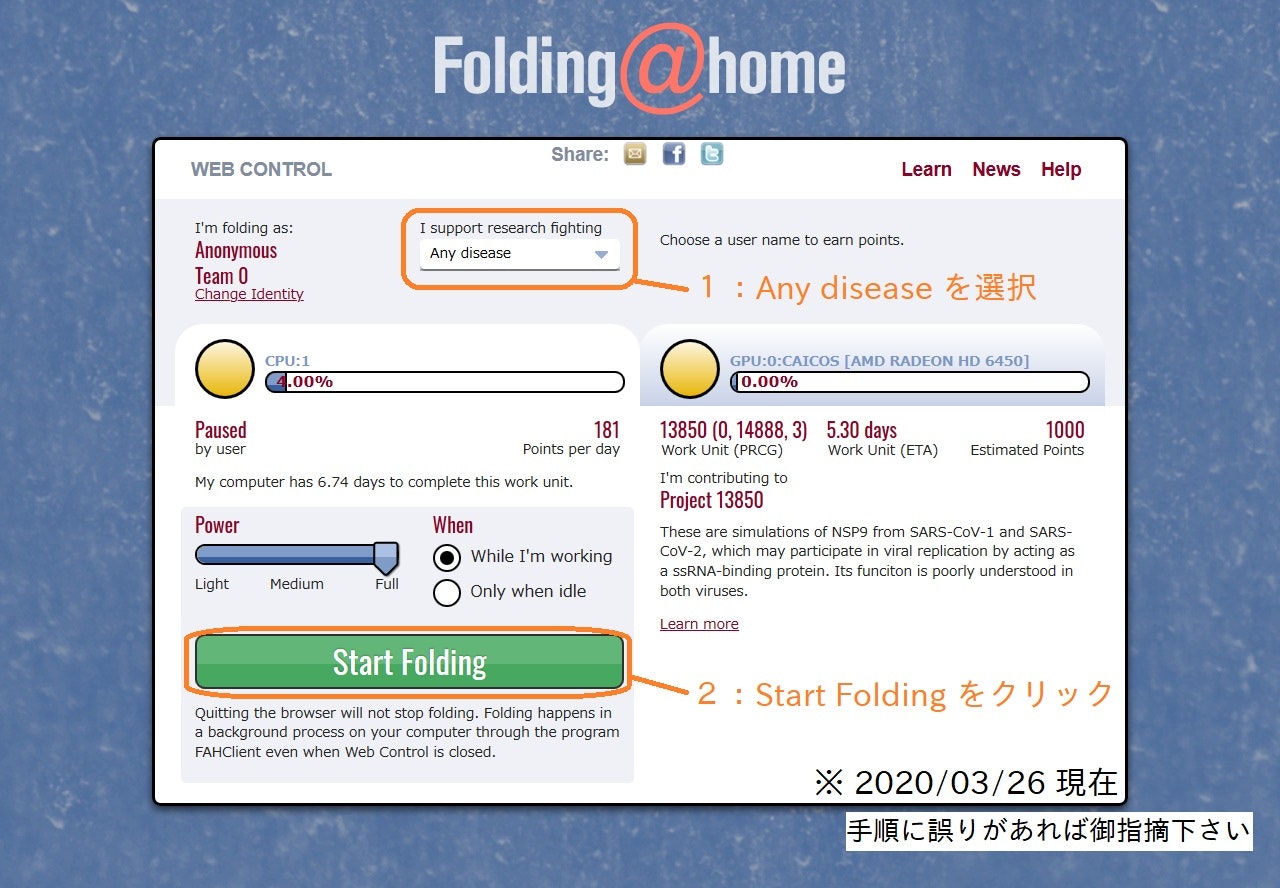
※ folding@home 開始後、https://client.foldingathome.org/ をブラウザで開く。
"I support research fighting" のプルダウンメニューで "Any disease" を指定することで COVID-19 関連プロジェクトに計算リソースを提供します。
3/27 現在、COVID-19 関連プロジェクトのみに計算リソースを提供することは出来ないそうです。
スクリーンショット(macOS / FreeBSD)
Folding@home の COVID-19 特設ページ
To focus on Covid19 research set your category to any.
Folding@home の COVID-19 関連 FAQ
- How do I choose to help with the COVID-19 related projects ?
To help in the fight against COVID-19, you need to select
- Webcontrol : "Any disease" in the list "I support research fighting"
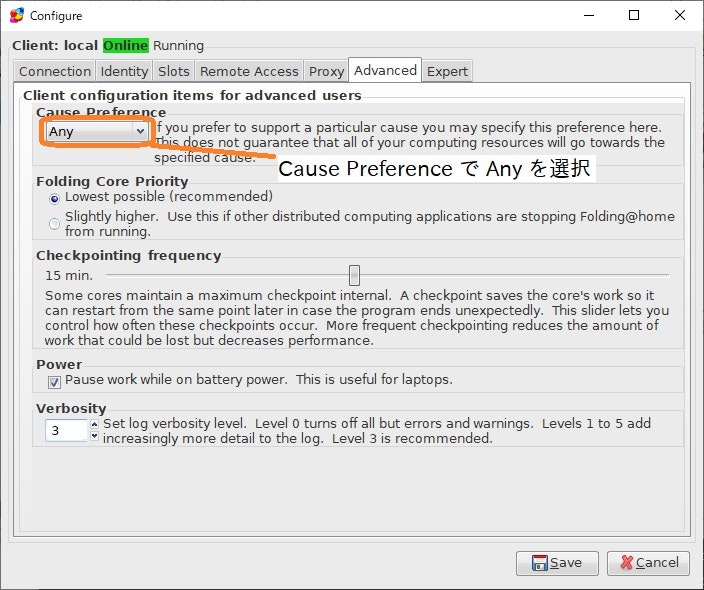
- Advanced Control/FAHControl : Configure > Advanced, select "Any" in the list "Cause Preference"
The COVID-19 related projects are on top priority and will be assigned automatically.
- Can I choose to work only on the COVID-19 related projects ?
No, you can't.
In FoldingHome, you never choose to work on only one project (or family of projects). The setting described above is a preference, but if no work is available to match your preferences, the system is designed to send you what need to be done at the time of your work request.
以下、上記のGoogle翻訳
- COVID-19関連プロジェクトの支援をどのように選択すればよいですか?
COVID-19との戦いを支援するには
-Webcontrol:「I support research fighting」リストで「Any disease」を選択
-Advanced Control / FAHControl:Configure > Advanced、「Cause Preference」リストで「Any」を選択
COVID-19関連プロジェクトは最優先事項であり、自動的に割り当てられます。
- COVID-19関連のプロジェクトでのみ作業することを選択できますか?
いいえ、できません。
FoldingHomeでは、1つのプロジェクト(またはプロジェクトのファミリー)だけで作業することを選択することはありません。 上記の設定は設定ですが、設定に一致する作業がない場合、システムは、作業要求時に実行する必要があることを送信するように設計されています。
Rosetta@home への参加
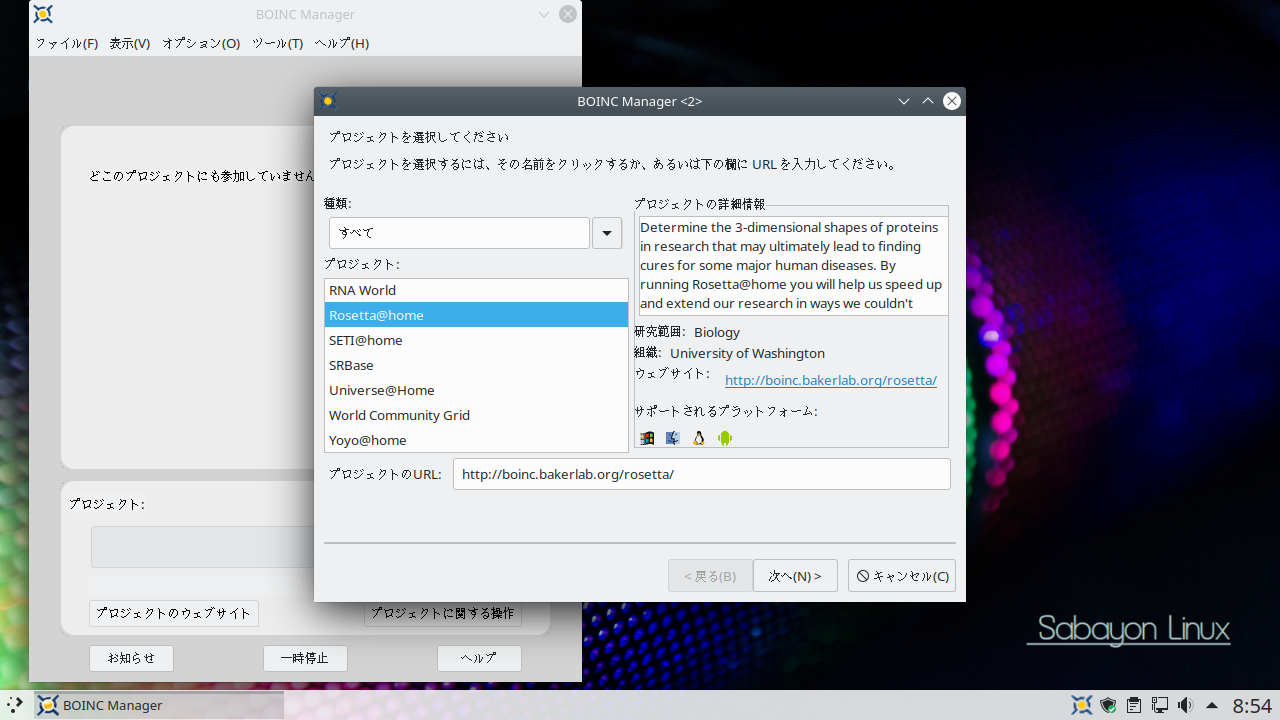
Rosetta@home への参加の流れ
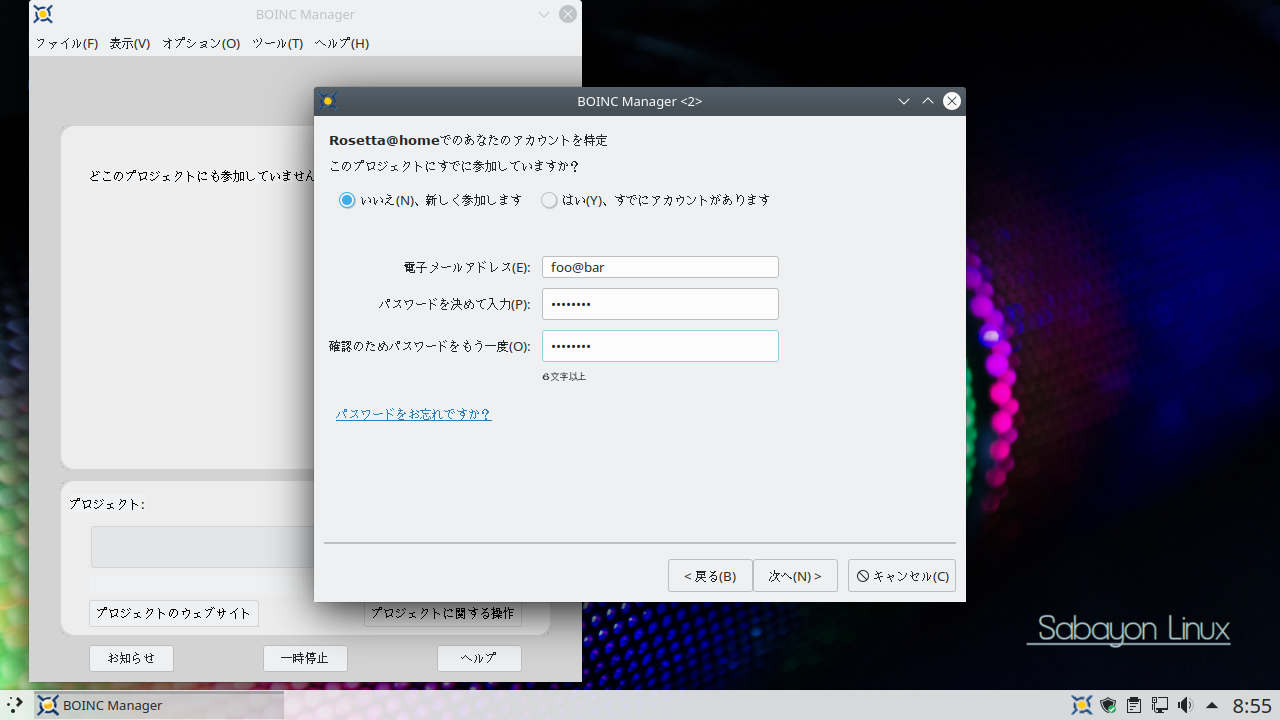
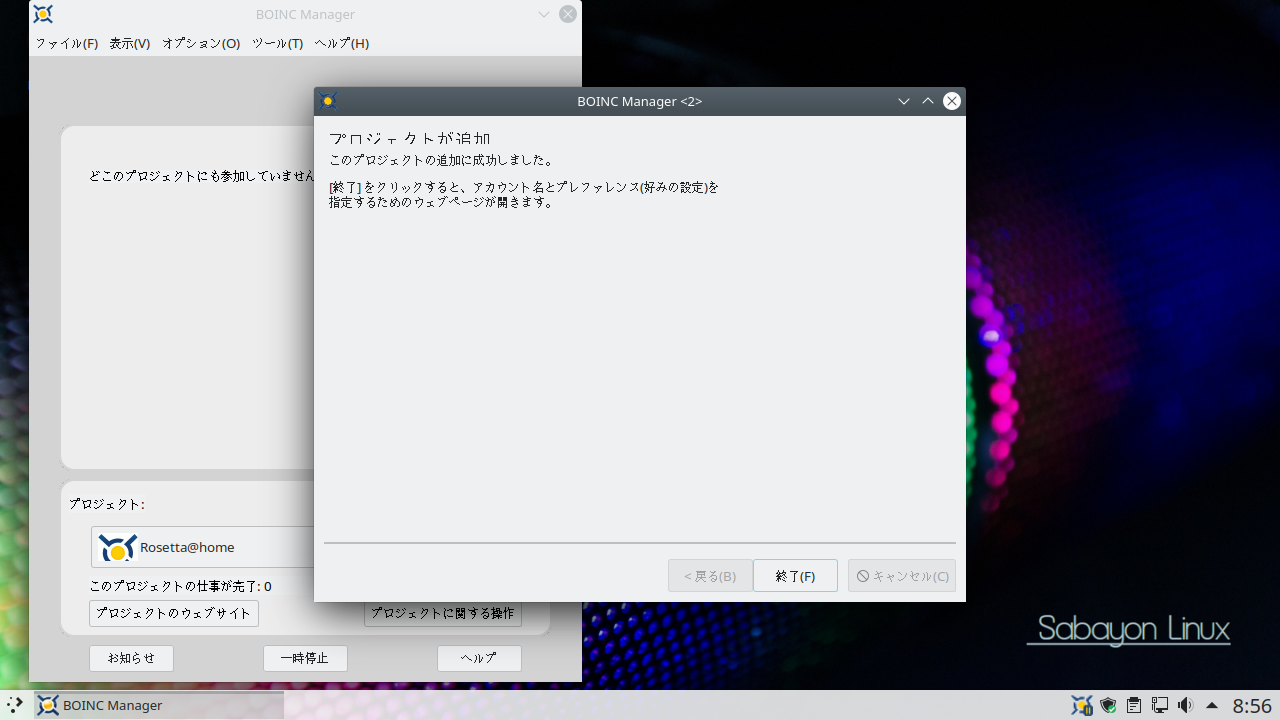
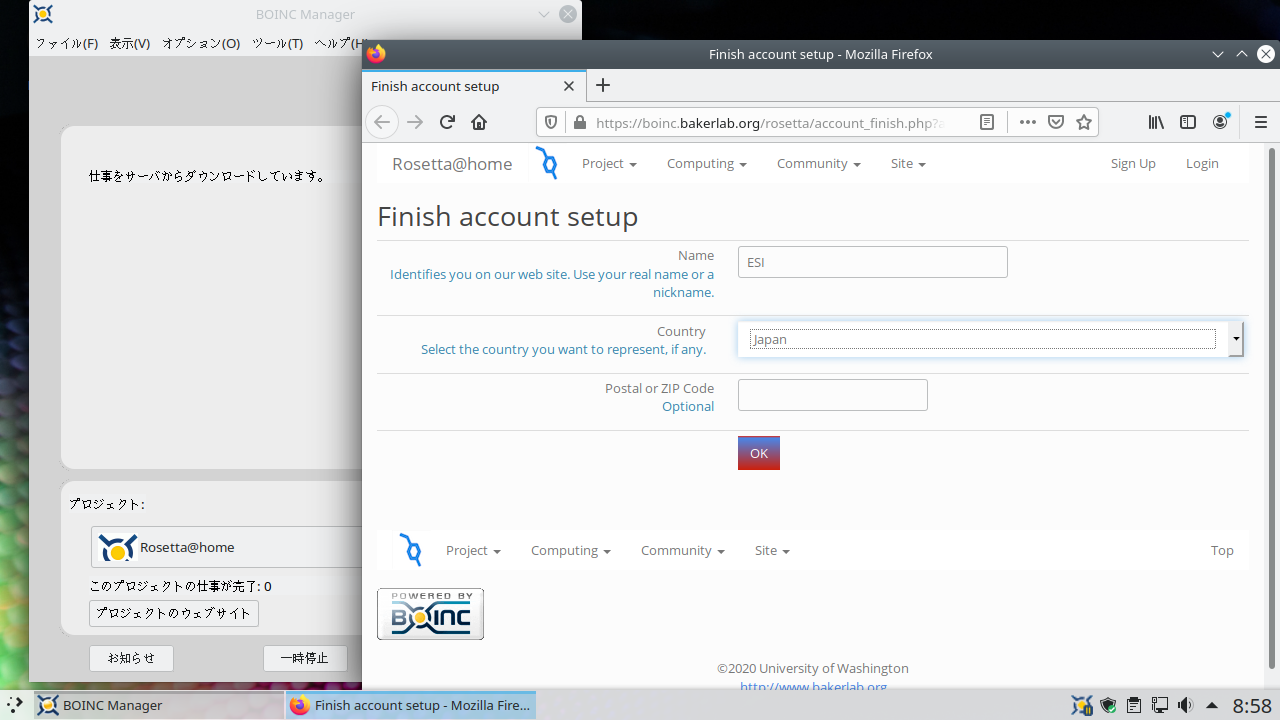
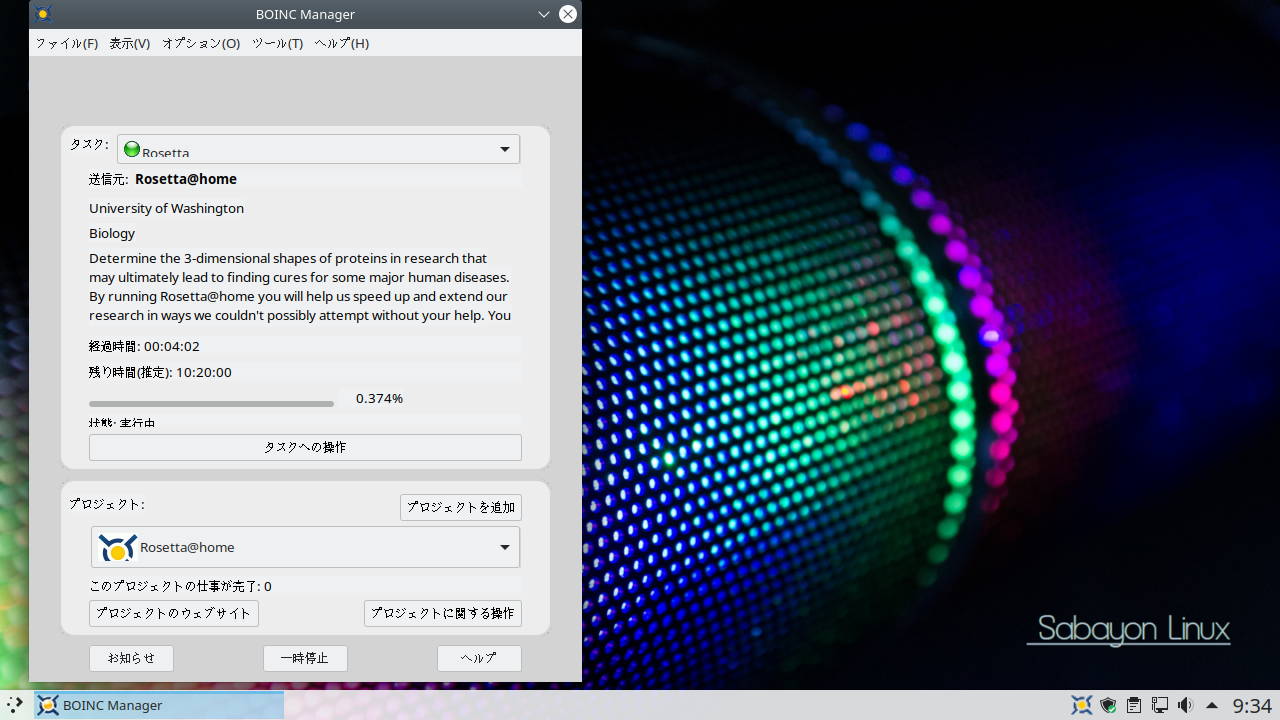

※ タスクへの操作 > グラフィックを表示 で作業中の分子のモデルを表示できます。
Android で参加する場合
※ Twitter のタイムラインによると、Android から Rosetta@home への参加はもしかすると上手く行かないかもしれません。
Rosetta's role in fighting coronavirus
Thank you to all R@h volunteers for your contributions to help accurately model important coronavirus proteins. The collective computing power that you provide through R@h helps academic research groups world wide model important protein structures like these.
From a recent IPD news post:
"We are happy to report that the Rosetta molecular modeling suite was recently used to accurately predict the atomic-scale structure of an important coronavirus protein weeks before it could be measured in the lab. Knowledge gained from studying this viral protein is now being used to guide the design of novel vaccines and antiviral drugs."
Since the release of SARS-CoV-2 genome sequences in late January, a number of important corona virus proteins like the one described above have been modeled on R@h volunteer computers. A list of these proteins is provided by the Seattle Structural Genomics Center for Infectious Disease (SSGCID).
24 Feb 2020, 18:19:59 UTC
以下、上記のGoogle翻訳
重要なコロナウイルスタンパク質を正確にモデル化するために貢献してくれたすべてのR @ hボランティアに感謝します。 R @ hを通じて提供する集合的なコンピューティング能力は、世界の学術研究グループがこれらのような重要なタンパク質構造をモデル化するのに役立ちます。
最近のIPDニュース投稿から:
「私たちは最近、ロゼッタ分子モデリングスイートが重要なコロナウイルスタンパク質の原子スケールの構造をラボで測定できるようになるまで正確に予測するために使用されたことを報告します。このウイルスタンパク質の研究から得られた知識は現在、 新しいワクチンと抗ウイルス薬の設計を導きなさい。」
1月下旬にSARS-CoV-2ゲノムシーケンスがリリースされて以来、上記のような多くの重要なコロナウイルスタンパク質がR @ hボランティアコンピューターでモデル化されています。 これらのタンパク質のリストは、シアトル構造感染症センター(SSGCID)によって提供されます。
2020年2月24日18:19:59 UTC